DNS

Petra Nordinghaus-Martin
AllgemeinesBiophysik, 1) Biophysik: Desoxyribonukleinsäuren, DNA (Abk. von engl. Deoxyribonucleic Acid), hochpolymere Nukleinsäuren aus 2¢-Desoxynukleotiden.
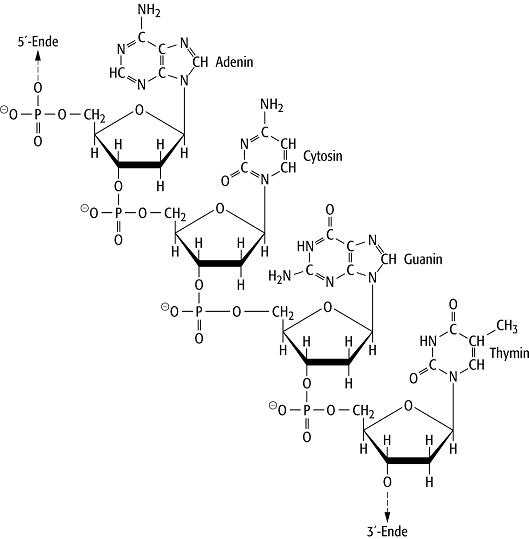
Chemische Struktur: Die DNS besteht aus linearen Kettenmolekülen, in denen als Monomere fast ausschliesslich vier verschiedene Standardnukleotide (2¢-Desoxyribonucleosidmonophosphate A, C, G, und T) in gebundener Form vorkommen (Abb. 1): dAMP (2¢-Desoxyadenosinmonophosphat, Adenin, A), dCMP (2¢-Desoxycytosinmonophosphat, Cytosin, C), dGMP (2¢-Desoxyguaninmonophosphat, Guanin, G) und dTMP (2¢-Desoxythymidinmonophosphat, Thymin, T). Die Zahl der Monomere in einem DNS-Molekül kann sehr grosse Werte annehmen und übersteigt alle von anderen Polymeren bekannten Grössenordnungen ( » 105 beim Bakteriophagen T2, Abb. 4, » 106 bei der Bakterie Escherichia coli und » 109 bei Säugetieren, im letzteren Falle ist die Gesamtlänge der DNS etwa 1 Meter, Biomakromoleküle). Raumstruktur und physikalische Eigenschaften: Die bestimmenden Faktoren der lokalen Raumstruktur der DNS sind 1) die hydrophoben Wechselwirkungen der benachbarten Nukleinsäurebasen eines Stranges (Stapelpackung der planaren Nukleinsäurebasen, "Stacking"), 2) Wasserstoffbrücken zwischen den funktionellen Gruppen der Nukleinsäurebasen sequentiell weit auseinanderliegender Nukleotide oder verschiedener Kettenmoleküle (Basenpaarung), 3) die elektrostatische Abstossung gleichgeladener Phosphatgruppen, 4) die hohe Zahl von Konformationsfreiheitsgraden der Zucker-Phosphat-Kette (flexibles Rückgrat). Dies sind die Ursachen, weshalb DNS zwar eine Sekundärstruktur, aber keine eigene Tertiärstruktur ausbildet.
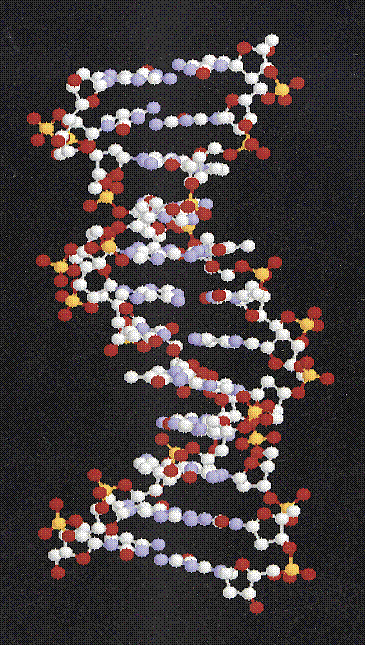
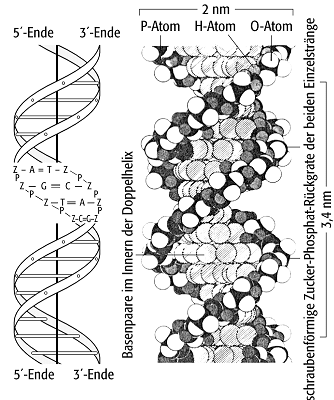
Ein DNS-Einzelstrang lagert sich beim Vorhandensein eines sogenannten komplementären DNS-Stranges an diesen an (Modell der doppelsträngigen Helix, Abb. 2 und 3). Der daraus entstehende Doppelstrang nimmt wegen des Kompromisses aus optimalem Stacking und möglichst geringer elektrostatischer Abstossung der Phosphate eine Helixstruktur an. Die funktionellen Gruppen der Nukleinsäurebasen unterschiedlicher Stränge werden dabei mit Wasserstoffbrücken abgesättigt.
Die durch die heterozyklischen Nukleinsäurebasen bedingte Absorption im UV-Bereich (bei 260 nm) wird häufig zum Nachweis der DNS mit Absorptionsspektroskopie genutzt. Die CD-Spektroskopie im gleichen Wellenlängenbereich ist ein einfaches Mittel zum Verfolgen der Denaturierung der DNS.
Biologische Bedeutung: Die nichtzufällige Sequenz der Monomere im DNS-Kettenmolekül dient als Speicher der genetischen Information sowohl bei allen ein- und mehrzelligen Organismen als auch bei Viren (genetischer Code, Abb. 4). Einzige Ausnahme bilden sogenannte RNS-Viren und Phagen, in denen der Genom in Form der Nukleotidsequenz von RNS verschlüsselt ist. Dabei verfügt bei mehrzelligen Organismen jede Zelle zumindest im Anfangsstadium ihrer Entwicklung über einen kompletten Satz der gesamten genetischen Information des Organismus. Das Modell der doppelsträngigen DNS-Helix erklärt, wie die DNS ihre biologische Aufgabe wahrnehmen kann: Durch die Paarung komplementärer Stränge ist es DNS-Reparatursystemen in vivo möglich, einen einzelnen beschädigten Strang, z.B. infolge der Einwirkung von ionisierender Strahlung, durch Vergleich mit dem Partnerstrang zu identifizieren und wiederherzustellen. Damit ist eine gewisse Sicherheit bei der Informationsspeicherung über grosse Zeiträume gewährleistet. Andererseits kann jeder der Stränge als Matrix für die Synthese neuer DNS dienen (Replikation). Dabei entstehen zwei neue Doppelspiralen, jede mit einem alten und einem neuen Strang. Die identischen Kopien der genetische Information stehen dann bei Zellteilung (oder Virusvermehrung) den Tochterzellen (oder den neuen Viren) zur Verfügung. [FE]
2) Elektronische Kommunikation: Domain Name System, Internet.
DNS 1: Schema der chemischen Struktur eines DNS-Stranges. Es wird ein Ausschnitt mit der Sequenz ACGT gezeigt.
DNS 2: Ball-Balken-Darstellung der antiparallelen doppelsträngigen Helix in B-Form des selbstkomplementären Dodekamers CCGGAATTCCGG (Struktur 1BNA aus der Brookhaven Protein Data Bank). Man beachte die beiden verschieden grossen, parallel zu den Zucker-Phosphat-Rückgraten (engl. backbone) verlaufenden Furchen, die als grosse bzw. kleine Furche bezeichnet werden. Durch diese sind die Nukleinsäurebasen trotz ihrer dichten Packung in erheblichem Masse für Liganden zugänglich. Damit ist das Abtasten der Basensequenz auch ohne Aufspaltung der Doppelhelix möglich. Das ist von grosser Bedeutung für die Wechselwirkung mit regulatorischen Proteinen (Repressoren, Aktivatoren), RNS-Polymerasen und Reparaturenzymen.
DNS 3: Schema der Struktur der Doppelhelix (B-Form). Links ist ein Ausschnitt von etwa zwei Windungen Länge dargestellt. Rechts davon ist ein Teil des linken Bildes als Kalottenmodell wiederholt.
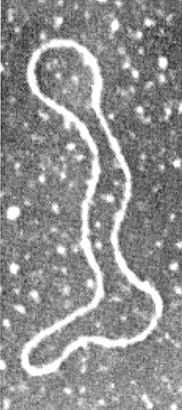
DNS 4: Elektronenmikroskopische Aufnahme des isolierten DNS-Moleküls des Bakteriophagen T2. Die Länge des Fadens beträgt 56 mm (etwa 180000 Basenpaare).
Techniklexikon.net
Das freie Technik-Lexikon. Fundierte Informationen zu allen Fachgebieten der Ingenieurwissenschaften, für Wissenschaftler, Studenten, Praktiker & alle Interessierten. Professionell dargeboten und kostenlos zugängig.
Techniklexikon
Modernes Studium der Physik sollte allen zugängig gemacht werden.