RNS

Irene Kramer-Schwenk
Biophysik, RNA, Ribonucleinsäure, hochpolymere lineare Kettenmoleküle (Biomakromoleküle), die als monomere Bausteine neben einigen seltenen Nucleotiden hauptsächlich vier Standard-Nucleotide besitzen: Adenosin-5\'-Monophosphorsäure (Abk. A), Cytidin-5\'-Monophosphorsäure (C), Guanosin-5\'-Monophosphorsäure (G) und Uracil-5\'-Monophosphorsäure (U) (siehe Abb.).
Unter physiologischen Bedingungen liegt RNS als Polyanion mit je einer negativen Ladung pro Monomer vor. Die Elektroneutralität sichern Kationen (Na+, K+), organische Ionen bzw. basische Proteine. Die Heterozyklen der Nucleinsäurebasen bedingen ein Absorptionsmaximum bei 260 nm (UV-Bereich), welches zur Konzentrationsbestimmung herangezogen werden kann.
Funktionell unterscheidet man neben mehreren Gruppen kleiner RNS-Moleküle vor allem 1) Boten-RNS (messenger RNS, mRNS), 2) ribosomale RNS (rRNS) und 3) Transport-RNS (transfer RNS, tRNS). Alle drei Klassen sind notwendig für die Translation, deshalb sind sie auch in allen Organismen vertreten. Der Polymerisationsgrad der Ribonucleinsäuren differiert stark. Am kleinsten sind die Transport-RNS (ca. 80 Nukleotide) und die kleineren ribosomalen RNS (80-130 Nucleotide, Ribosom). Grössere ribosomale RNS erreichen eine Länge von 1 500-4 000 Nucleotiden, messenger RNS können bis zu 104 Nukleotide und mehr haben. Die Synthese von RNS findet an der Matrix der Gene in der DNS statt (Transkription), gefolgt von einer Reifung der primären Transkripte (Splicing). Die tRNS und rRNS existieren meist über mehrere Zellzyklen hinweg, die Halbwertszeit der mRNS liegt dagegen im Minutenbereich (Hydrolyse nach der Translation). Bei einigen Viren und Bakteriophagen ist das Genom in RNS-Form vorliegend. RNS kann katalytische Aktivität haben.
RNS-Moleküle können intramolekulare doppelspiralige Abschnitte in der A-helikalen Konformation ausbilden, welche der DNS-Doppelspirale entsprechen. Zwischen den Doppelspiralen befinden sich Schleifen (Loops), welche sich im Falle der tRNS und rRNS zu einer eigenen Tertiärstruktur packen. Dabei ist die Entstehung von Pseudoknoten möglich. Dagegen verbleibt mRNS vorrangig im sekundärstrukturlosen Einzelstrang, u.a. auch wegen der Wechselwirkung mit Proteinen; einzelne doppelsträngige Bereiche der mRNS haben regulatorische Bedeutung, weil sie zeitweilig die Translation blockieren.
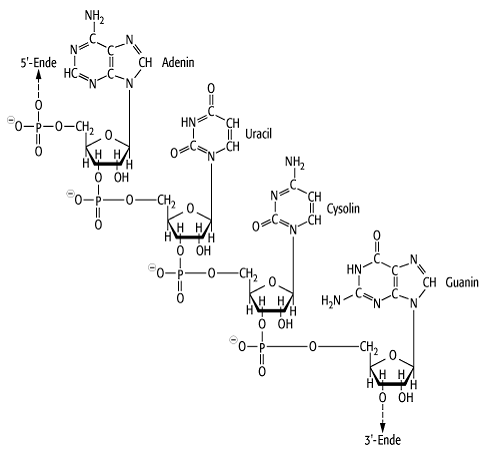
RNS: Ausschnitt aus dem Strang einer Ribonucleinsäure. Der
Ausschnitt zeigt die Basensequenz AUCG in der konventionellen Richtung 5\' ![]() 3\'.
3\'.
Techniklexikon.net
Das freie Technik-Lexikon. Fundierte Informationen zu allen Fachgebieten der Ingenieurwissenschaften, für Wissenschaftler, Studenten, Praktiker & alle Interessierten. Professionell dargeboten und kostenlos zugängig.
Techniklexikon
Modernes Studium der Physik sollte allen zugängig gemacht werden.